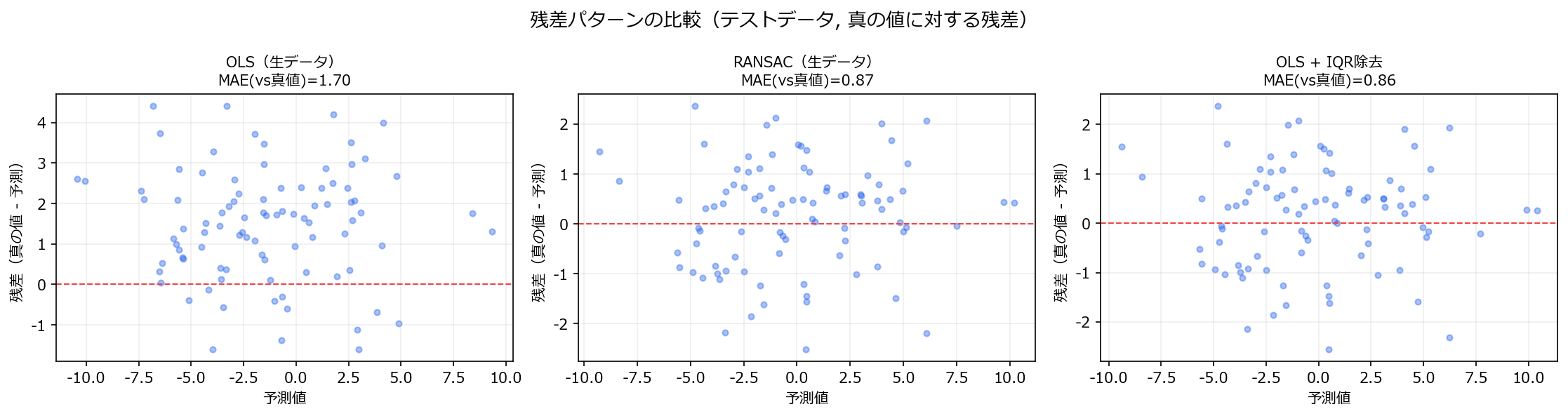
1
2
3
4
5
6
7
8
9
10
11
12
13
14
15
16
17
18
19
20
21
22
23
24
25
26
27
28
29
30
31
32
33
34
35
36
37
38
39
40
41
42
43
44
45
46
47
48
49
50
51
52
53
54
55
56
57
58
59
60
61
62
63
64
65
66
67
68
69
70
71
72
73
74
75
76
77
78
79
80
81
82
83
84
85
86
87
88
89
90
91
92
93
94
95
96
97
| from sklearn.model_selection import cross_val_score, KFold
from sklearn.linear_model import LinearRegression, Ridge, RANSACRegressor, HuberRegressor, TheilSenRegressor
from sklearn.base import clone
from scipy.stats import mstats
import seaborn as sns
cv = KFold(n_splits=5, shuffle=True, random_state=42)
models = {
"OLS": LinearRegression(),
"Ridge": Ridge(alpha=1.0),
"RANSAC": RANSACRegressor(estimator=LinearRegression(), random_state=42),
"Huber": HuberRegressor(epsilon=1.35),
"TheilSen": TheilSenRegressor(random_state=42),
}
def iqr_filter(X, y):
q1, q3 = np.percentile(y, 25), np.percentile(y, 75)
iqr = q3 - q1
mask = (y >= q1 - 1.5 * iqr) & (y <= q3 + 1.5 * iqr)
return X[mask], y[mask]
def winsorize(y, pct=0.05):
lower = np.percentile(y, pct * 100)
upper = np.percentile(y, (1 - pct) * 100)
return np.clip(y, lower, upper)
preprocs = {
"なし": lambda X, y: (X, y),
"IQR除去": iqr_filter,
"Winsorize(5%)": lambda X, y: (X, winsorize(y)),
}
results = []
for prep_name, prep_fn in preprocs.items():
for mdl_name, mdl in models.items():
maes, coef_bias = [], []
for train_idx, test_idx in cv.split(X):
X_tr, X_te = X[train_idx], X[test_idx]
y_tr, y_te = y[train_idx], y[test_idx]
X_pp, y_pp = prep_fn(X_tr, y_tr)
m = clone(mdl)
try:
m.fit(X_pp, y_pp)
pred = m.predict(X_te)
maes.append(np.mean(np.abs(y_te - pred)))
# 係数バイアス
if hasattr(m, "coef_"):
coefs = m.coef_.ravel()[:2] if len(m.coef_.ravel()) >= 2 else m.coef_.ravel()
elif hasattr(m, "estimator_") and hasattr(m.estimator_, "coef_"):
coefs = m.estimator_.coef_.ravel()[:2]
else:
coefs = [np.nan, np.nan]
true_coefs = np.array([2.0, 3.0])
bias = np.mean(np.abs(coefs[:2] - true_coefs[:2]))
coef_bias.append(bias)
except Exception:
maes.append(np.nan)
coef_bias.append(np.nan)
results.append({
"前処理": prep_name, "モデル": mdl_name,
"MAE": np.nanmean(maes),
"係数バイアス": np.nanmean(coef_bias),
})
df_res = pd.DataFrame(results)
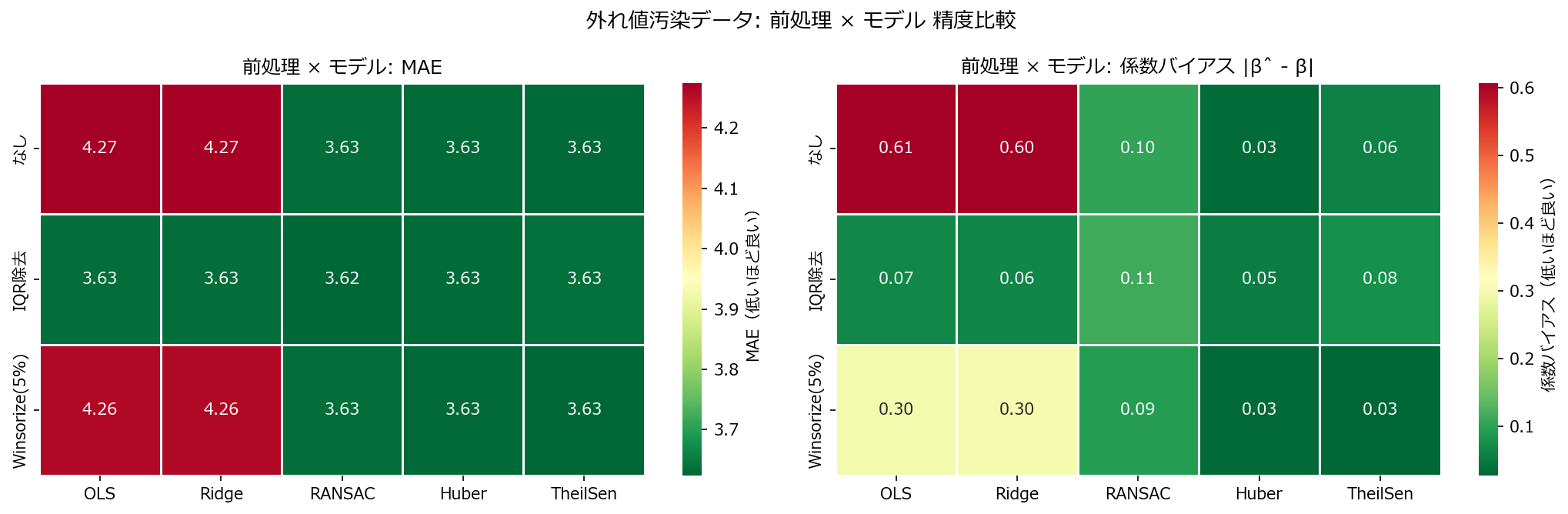
fig, axes = plt.subplots(1, 2, figsize=(14, 4.5))
pivot_mae = df_res.pivot_table(index="前処理", columns="モデル", values="MAE")
prep_order = ["なし", "IQR除去", "Winsorize(5%)"]
mdl_order = ["OLS", "Ridge", "RANSAC", "Huber", "TheilSen"]
pivot_mae = pivot_mae.reindex(index=[p for p in prep_order if p in pivot_mae.index],
columns=[m for m in mdl_order if m in pivot_mae.columns])
sns.heatmap(pivot_mae, annot=True, fmt=".2f", cmap="RdYlGn_r",
linewidths=0.5, ax=axes[0], cbar_kws={"label": "MAE(低いほど良い)"})
axes[0].set_title("前処理 × モデル: MAE")
axes[0].set_xlabel("")
axes[0].set_ylabel("")
pivot_bias = df_res.pivot_table(index="前処理", columns="モデル", values="係数バイアス")
pivot_bias = pivot_bias.reindex(index=[p for p in prep_order if p in pivot_bias.index],
columns=[m for m in mdl_order if m in pivot_bias.columns])
sns.heatmap(pivot_bias, annot=True, fmt=".2f", cmap="RdYlGn_r",
linewidths=0.5, ax=axes[1], cbar_kws={"label": "係数バイアス(低いほど良い)"})
axes[1].set_title("前処理 × モデル: 係数バイアス |β̂ - β|")
axes[1].set_xlabel("")
axes[1].set_ylabel("")
fig.suptitle("外れ値汚染データ: 前処理 × モデル 精度比較", fontsize=13)
fig.tight_layout()
plt.show()
|