2.9.2
การตรวจจับความผิดปกติ ②
สรุป
- สรุปเป้าหมาย สมมติฐาน และเงื่อนไขที่เหมาะสมของวิธีนี้.
- ตรวจสอบว่ากฎการอัปเดตหรือเกณฑ์การแบ่งส่งผลต่อพฤติกรรมโมเดลอย่างไร.
- ใช้ตัวอย่างโค้ดเพื่อกำหนดแนวทางปรับพารามิเตอร์อย่างเป็นรูปธรรม.
สัญชาตญาณ #
การตรวจจับความผิดปกติ ② ควรเข้าใจผ่านสมมติฐาน กลไกการปรับปรุงโมเดล และรูปแบบความผิดพลาดบนข้อมูลจริง เพื่อให้เลือกโมเดลและปรับพารามิเตอร์ได้อย่างเหมาะสม.
คำอธิบายโดยละเอียด #
1. เตรียมข้อมูลทดลอง #
เพิ่มคอลัมน์ใหม่ให้ข้อมูลเซนเซอร์เดิม เพื่อให้เป็นข้อมูล 2 มิติ
| |
| |
2. แนวคิดของการตรวจจับแบบหลายมิติ #
- มิติเดียว จะดู outlier ของฟีเจอร์นั้น ๆ
- หลายมิติ จะดูจุดที่ “ความสัมพันธ์ระหว่างฟีเจอร์” ผิดปกติ
ตัวอย่าง:
valueและvalue2ดูปกติทีละตัว → ปกติ- แต่ความสัมพันธ์ระหว่างสองตัวผิดปกติ → ผิดปกติ
3. วิธีที่ใช้ในตัวอย่าง #
ทดลอง 3 วิธีหลัก
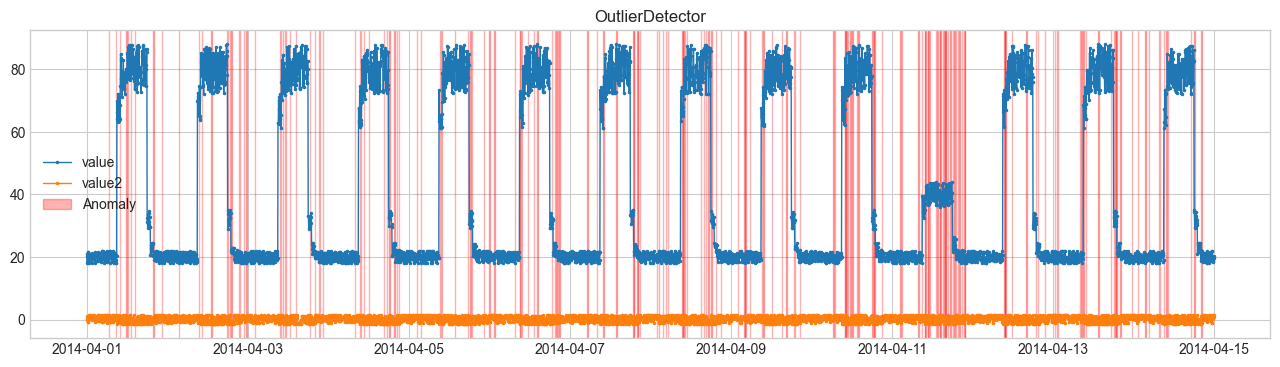
(1) OutlierDetector (LOF) #
ใช้ Local Outlier Factor (LOF)
วัดความหนาแน่นเฉพาะจุดเพื่อบอกว่าเป็น outlier หรือไม่
\(\text{lrd}\) คือ local reachability density
ค่า LOF สูง → จุดนั้น “โดดเดี่ยว” จากเพื่อนบ้าน
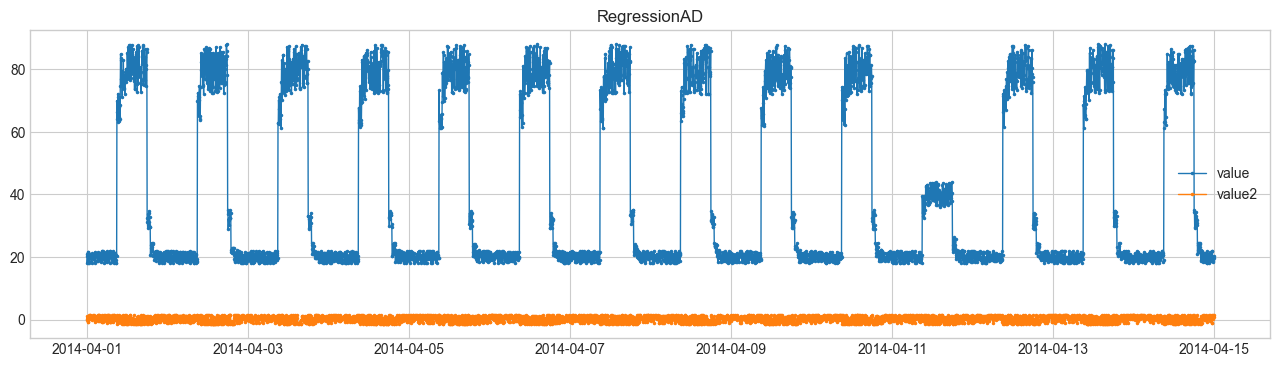
(2) RegressionAD (ความคลาดเคลื่อนจากรีเกรสชัน) #
ทำนายฟีเจอร์หนึ่ง (เช่น value2) จากฟีเจอร์อื่น แล้วใช้ความคลาดเคลื่อนเป็นสัญญาณผิดปกติ
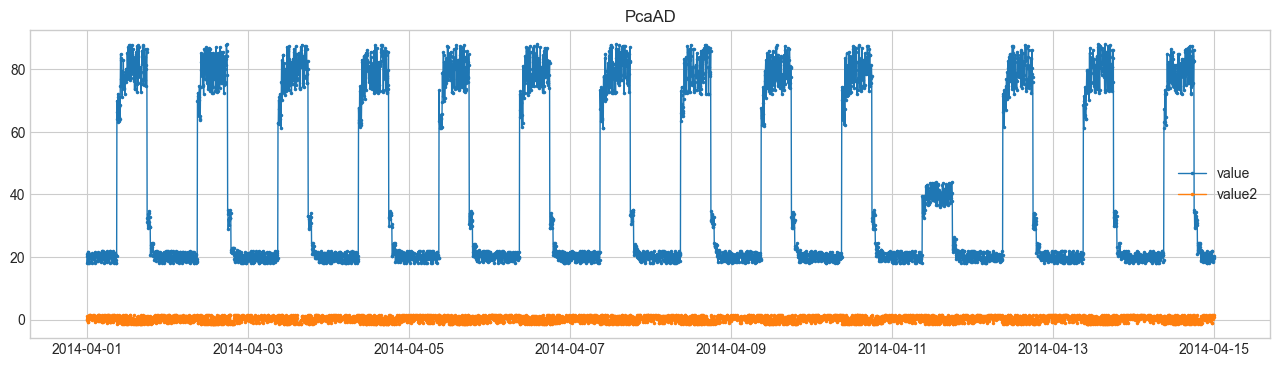
(3) PcaAD (PCA) #
ลดมิติด้วย PCA แล้วมองจุดที่ไม่สามารถอธิบายในมิติลดรูปได้
- แยกองค์ประกอบหลักของเมทริกซ์ \(X\)
- ดูค่าคลาดเคลื่อนหลังการสร้างกลับ $$ \| X - X_{\text{reconstructed}} \| > \text{threshold} $$
4. โค้ดทดลอง #
| |
5. การแสดงผล #